Do, 09.04.2026 — Redaktion
Als vor einem Vierteljahrhundert die vollständige Sequenzierung des menschlichen Genoms und damit die Identifizierung aller Gene gelang, dachte man, dass man in Kürze auch deren Funktion besser verstehen werde. Man erwartete dann auch zu entdecken, welche Rolle einzelne Gene bei den global dominierenden nicht-übertragbaren Erkrankungen spielen. Die Hoffnung hier bald Prävention und zielführendere Therapien entwickeln zu können wich der Ernüchterung: die Genetik erklärt einen Teil des Geschehens, nicht-genetische Faktoren – individuelle Umwelteinflüsse, denen wir ausgesetzt sind und wie diese (Stoffwechsel)Prozesse im Körper beeinflussen - können offensichtlich einen wesentlichen Einfluss auf das Erkrankungsrisiko haben. Dies zeigt die bislang wohl umfangreichste Studie über Assoziationen zwischen umweltbedingten Expositionen und gesundheitlichen Folgen, die kürzlich veröffentlicht wurde und wegweisend für die künftige Exposomforschung sein dürfte.
Das Exposom-Konzept
Die neue Vorgangsweise des Humanen Genom Projekts hinsichtlich Methodik, internationaler Zusammenarbeit und rechnergestützter Bewältigung der anfallenden enormen Datenmengen haben den Weg zu einer neuen Ära der Biowissenschaften eingeleitet, der Systembiologie. Diese versucht Systeme als Gesamtheit (gekennzeichnet durch das Suffix -om), d.i. in ihrer Struktur, Dynamik und Interaktion zwischen den Komponenten zu erfassen. Neben dem Genom sind u.a das Proteom für die Gesamtheit der Proteine und ihrer Interaktionen in einem System (Zelle, Organismus) zu nennen, das Metabolom für die Gesamtheit der Stoffwechselprozesse und -produkte, das Phänom für die Gesamtheit der beobachtbaren veränderlichen Merkmale (Phänotypen) eines Organismus und auch das überaus komplexe Exposom.
- Der Begriff Exposom wurde erstmals von dem Onkologen Christopher Wild in einer 2005 veröffentlichten Arbeit „Complementing the Genome with an “Exposome”: The Outstanding Challenge of Environmental Exposure Measurement in Molecular Epidemiology.“ geprägt. Exposom steht als Ergänzung zum Genom für „die Gesamtheit der Umwelteinflüsse, denen der Mensch von der Zeugung an über die gesamte Lebensspanne ausgesetzt ist.“ Das Exposom-Konzept bedeutet eine umfassende Integration von externen und internen Faktoren, von:
- externen Faktoren physischer Art wie Chemikalien, Strahlung, Luftverschmutzung, Lärm, Klima;
- externen Faktoren sozial/Lifestyle-bedingter Art wie Ernährung, Stress, Genussmittel, Wohnumfeld, Bildung;
- internen biologischen Faktoren wie Körperbau, Entzündungswerte, oxidativer Stress, Hormonstatus, Alterung, Mikrobiom.
Ein unmöglicher Ansatz auf dem Weg zur Realisierung
Anfänglich wurde der Ansatz jeden Umweltaspekt eines Individuums berücksichtigen zu wollen, als völlig unmöglich erachtet. Mit der Errichtung großer prospektiver Kohortenstudien mit eigenen Biobanken erschien das Exposom-Konzept in einem neuen Licht und begann sich ab 2010 zu einem rasant wachsenden, hochkomplexen Forschungsgebiet zu entwickeln. Eine Pionierrolle spielt(e) dabei die 2003 gegründete UK Biobank (https://www.ukbiobank.ac.uk/), die Forschern den weltweit umfassendsten anonymisierten Datensatz an gesundheitsbezogenen Daten (u.a. zu Lebensstil, Umwelt, körperlichen Messungen, Blutbestandteilen, Genetik, Gehirn-, Körper-und Knochenscans, Biomarkerdaten) und biologische Proben (Rund 17 Millionen Speichel-, Blut-, Urinproben) von einer halben Million freiwilligen Teilnehmern aus Großbritannien zur Verfügung stellt. Seit der Freigabe für die Forschung im Jahr 2012 wurden mehr als 18.000 peer-reviewte wissenschaftliche Arbeiten unter Verwendung von UK Biobank-Daten veröffentlicht.
Auch in anderen Regionen wachsen derartige Sammlungen von biologischen Proben, Gesundheitsakten und Umfragedaten (z.B. China Kadoorie Biobank, die All of Us Bank der NIH, die Biobank der Med Uni Graz). Dazu können Forscher nun auch auf Satellitendaten zu einer Vielfalt von lokalen Umweltexpositionen zurückgreifen.
In den letzten Jahren sind umfangreiche und insbesondere von der Europäischen Kommission und den US National Institutes of (Environmental)Health (NIH, NIEHS) nachhaltig finanzierte Initiativen der Exposomforschung entstanden.
Von der EU-geförderte Initiativen:
- Das 2020 von der EU mit über 100 Mio € geförderte European Human Exposome Network (EHEN) ist der weltweit größte Cluster mit neun großen Forschungsprojekten. https://www.humanexposome.eu/
- Auf EHEN baut das International Human Exposome Network (IHEN) auf – ein weltweites Netzwerk, das Standards und Methoden der Exposom-Forschung harmonisiert. https://humanexposome.net//
- Die 2022 von der Europäischen Kommission gestartete Initiative EIRENE RI (Research Infrastructure for Environmental Exposure Assessment in Europe) hat die systematische Kartierung des menschlichen Exposoms zum Ziel. Es soll eine dauerhafte Infrastruktur von Proben und Datenbanken entstehen. Mehr als 50 Institutionen aus 19 europäischen Ländern (darunter die Universität Wien) und 4 weiteren Mitgliedsländern (Japan, USA, Kanada, Australien) sind beteiligt. https://eirene.eu/
Von den US National Institutes of (Environmental)Health (NIH, NIEHS) geförderte Initiativen:
- Das bereits 2013 an der Emory University gegründete HERCULES Center https://emoryhercules.com/ („The Exposome: Erfassung der Gesamtheit der Umweltbelastungen im Laufe des Lebens, um den Beitrag der Umwelt zu Gesundheit und Krankheit besser zu verstehen.“)
- Die 2019 erfolgte Human Health Exposure Analysis Resource (HHEAR) Initiative bestehend aus 3 Komponenten: einem Netzwerk an Labors für Expositionsanalysen, einem Datenarchiv und Datenstandards, einem Koordinierungszentrum. https://hhearprogram.org/
- Im Oktober 2024 startete das NIH-weite Network for Exposomics in the United States (NEXUS) (https://www.nexus-exposomics.org/. NEXUS arbeitet auch mit anderen Exposom-Koordinierungszentren zusammen, u.a. mit EIRENE und IHEN (siehe oben). Mission Statement von NEXUS: „Unsere Mission ist es, die Sichtweise der biomedizinischen und gesundheitspolitischen Fachkreise auf umweltbedingte Krankheitsfaktoren zu revolutionieren, indem wir neue Instrumente, Forschungsnetzwerke und Methoden entwickeln, die die Exposomik zu einem zentralen Bestandteil der wissenschaftlichen und biomedizinischen Forschung machen.“ Aus der NEXUS-Initiative kommt die unten beschriebene neue Studie – Hauptautor ist Chirag Patel, ein führender Exposomforscher und einer der Leiter von Nexus –, die die Zusammenhänge zwischen vielen Umweltbelastungen und gesundheitlichen Ergebnissen gleichzeitig und systematisch untersucht – ein Schritt zu einem Human Exposome Project.
Eine bahnbrechende Studie
Im März 2026 ist im Fachjournal Nature Medicine die bislang wohl umfangreichste Studie über Assoziationen zwischen umweltbedingten Expositionen und gesundheitlichen Folgen unter dem Titel „Ein Atlas der Zusammenhänge zwischen Exposom und Phänotypen in Gesundheit und Erkrankungsrisiko“ erschienen [1]. Der Studie liegen gesundheitsbezogene Daten aus jährlichen Erhebungen des National Health and Nutrition Examination Survey (NHANES) zwischen 1999 und 2018 zugrunde (durchgeführt vom National Center for Health Statistics).
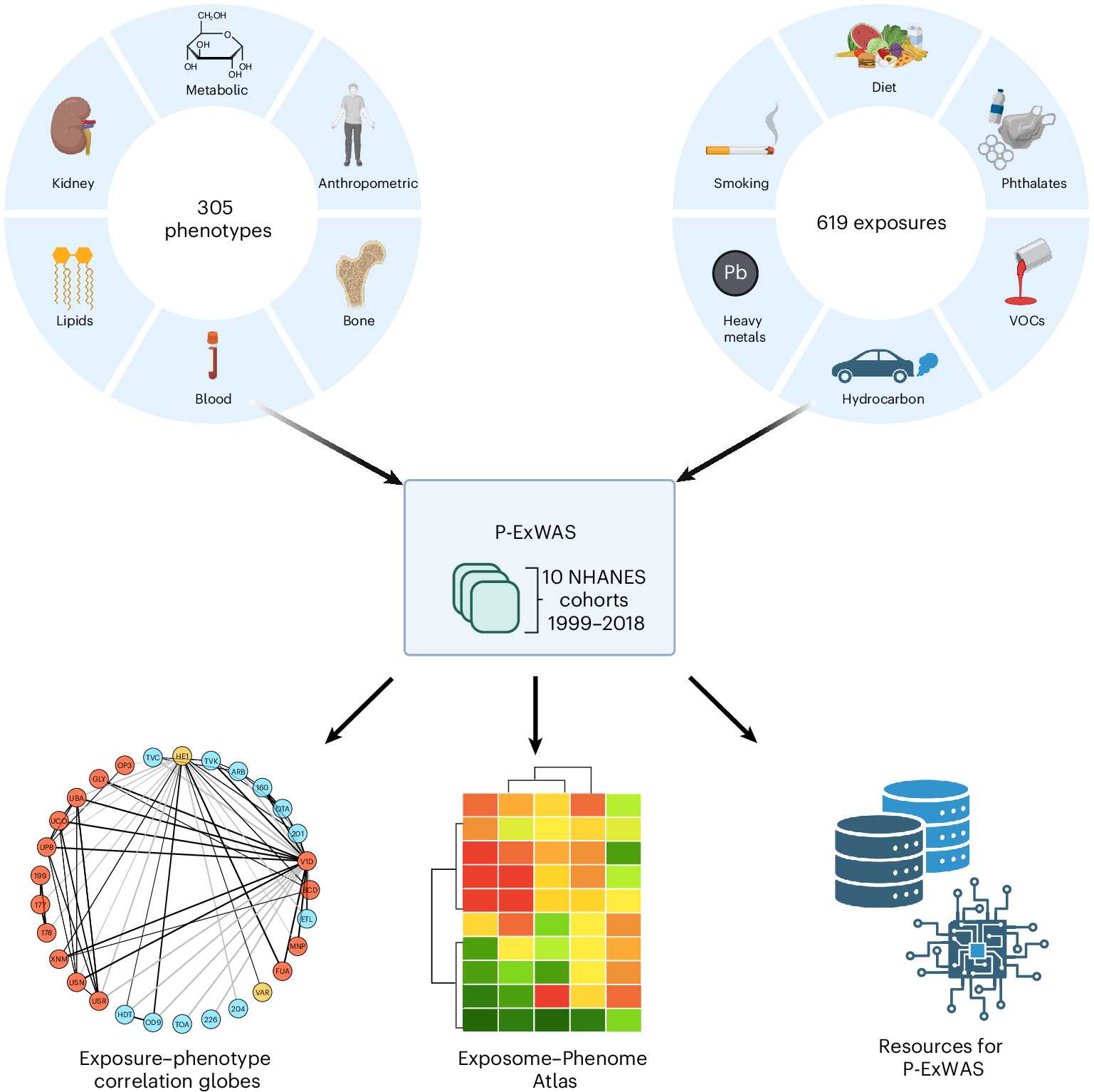
| Abbildung 1. Schema der systematischen Assoziierung Exposom – Phänom (P ExWAS). Oben links: Beispiele aus dem Bereich von 305 Phänotypen. Oben rechts: Beispiele aus dem Bereich von 619 Expositionen. Die Daten wurden über Kohortenstichproben der NHANES 1999–2018 (Mitte) hinweg harmonisiert. Unten: Von Ch. Patel & Arjun K. Manray entwickelte Ressourcen zur Beschreibung der Exposom-Phänom Assoziationen: Correlation globes [2], der Exposome-Phänom-Atlas und digitale Ressourcen (Datenbank und Software). (Quelle: Fig.1. aus Patel et al., 2026, [1]. https://doi.org/10.1038/s41591-026-04266-0. License: cc-by.) |
Waren bislang epidemiologische Studien auf die Auswirkungen eines oder weniger Umweltfaktoren zumeist auf eine einzelne Erkrankung beschränkt, so wurden nun mehr als 115.000 Assoziationen zwischen 619 Umweltexpositionen und 305 klinisch relevanten gesundheitlichen Ergebnissen (Phänotypen) gleichzeitig getestet. Der Erstautor Chirag Patel und Arjun K. Manray – beide Bioinformatiker, Professoren in Harvard Medical School - hatten zuvor (in Anlehnung an die genomweiten Assoziationsstudien GWAS) rechnergestützte „exposome-wide association studies“ (ExWAS) entwickelt, die zur Auffindung und Bestätigung von Zusammenhängen zwischen Expositionen und Phänotypen angewandt werden [2]. Die 619 Expositionen umfassten in 18 Kategorien diverse Schadstoffe (darunter auch die aus Studien wie auch aus Medien besonders bekannt gewordenen "Ewigkeitschemikalien", Weichmacher oder flüchtige organische Verbindungen), Nährstoffe, Supplemente und Infektion, während 305 Phänotypen in 18 Kategorien u.a. den Body-Mass-Index, den Blutzuckerspiegel, Lipidstoffwechsel, Entzündung, Nieren- und Lungenfunktion umfassten (zu den Kategorien: siehe Abbildung 2). Ein vereinfachtes Schema der Studie ist in Abbildung 1 dargestellt.
Die Ergebnisse lassen sich kurz umreißen:
- Es wurde offensichtlich keine „smoking gun“ gefunden – also kein Faktor (Schadstoff, Nahrungsbestandteil), der für sich allein als Treiber einer Krankheit fungieren würde.
- Von den insgesamt mehr als 100 000 getesteten Assoziationen erwiesen sich mehr als 5600 als statistisch signifikant. Auch in diesen Fällen waren die Auswirkungen einzelner Expositionen auf die Phänotypen äußerst bescheiden: über Hunderte von Phänotypen hinweg konnte damit weniger als 1 Prozent der Varianz zwischen verschiedenen Personen erklärt werden.
- Wurden allerdings bis zu 20 Expositionen gleichzeitig berücksichtigt, so konnten im Durchschnitt 3,5 % der Varianz - vergleichbar mit dem Risiko einzelner genetischer Varianten - erklärt werden. Traten bestimmte Mischungen von Expositionen auf, beispielsweise 20 Faktoren, die u.a Transfette, „Ewigkeitsmoleküle“ und Vitamin E-Formen erfassten, so erklärten sie 43 % der Variation im Triglyceridspiegel, dem bekannten Risikofaktor von Herz-Kreislauferkrankungen.
- Eine objektive Messung ist unabdingbar: Die Bestimmung von Biomarkern (z.B. von Nährstoff- oder Tabak-Metaboliten im Serum) ergab Assoziationen, welche die selbstberichtete Anamnese der Teilnehmer (auf Fragebögen) nicht erfasste.
Der Exposom-Phänom Atlas
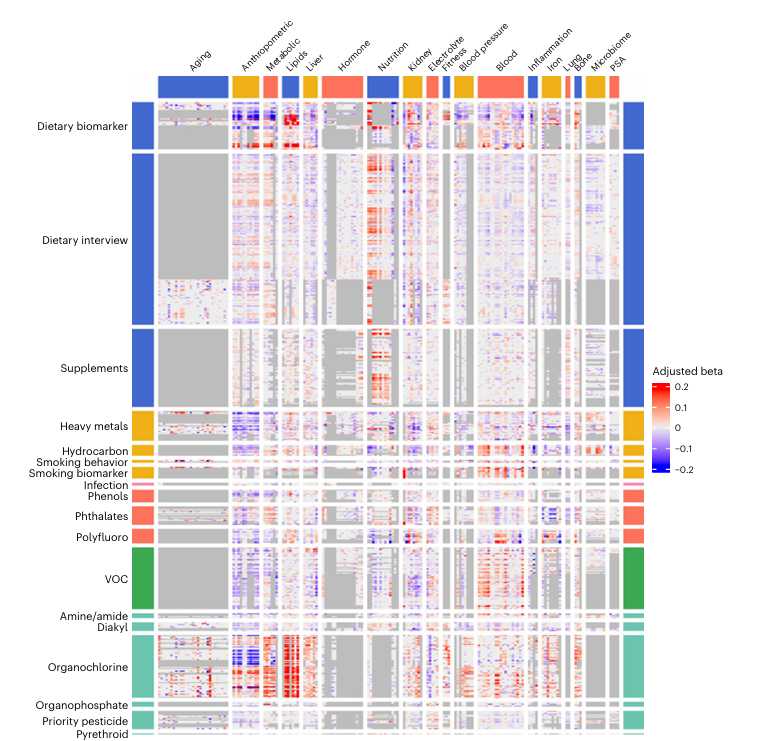
| Abbildung 2 S Der Exposom-Phänom Atlas. Matrix aus 625 Expositionen und 305 Phänotypen. Heatmap mit dem standadisierten Regressionskoeffzienten (von blau nach rot), graue Felder: Assoziation konnte nicht geschätzt werden. (Bild: Fig. 4 aus [1]. Patel et al., 2026, https://doi.org/10.1038/s41591-026-04266-0. License: cc-by.) |
Einen Eindruck von dem im Studientitel genannten Atlas gibt Abbildung 2. Ohne ins Detail gehen zu wollen, ist in Form einer Heatmap eine Matrix aus 305 Phänotypen (in 18 Kategorien) als Spalten dargestellt und 625 Expositionen (in 18 Kategorien) als Zeilen. Jedes Feld der Matrix enthält die lineare Assoziation zwischen einer Exposition und einem Phänotyp, angegeben in „adjusted beta“, dem standardisierten Regressionskoeffizienten. Daten und Software sind für andere Forschergruppen frei zugänglich.
Die Ergebnisse zeigen, wie wichtig es ist, umweltbedingte Krankheitsrisiken nicht isoliert sondern in ihrer Gesamtheit zu untersuchen. Unser Erkrankungsrisiko kann nicht durch eine einfache „Ursache-Wirkungs-Beziehung“ eines einzelnen Faktors dargestellt werden; neben den vererbten Grundlagen spiegelt es vielmehr den kumulativen Effekt von Vielfach-Belastungen aus der Umwelt wieder, die in Kombination zu Synergien, verstärkten Auswirkungen führen können.
Die Studie ist zweifellos wegweisend für die künftige Exposomforschung. Den Autoren ist bewusst, dass sie nur einen Bruchteil der Expositionen und Phänotypen getestet haben; sie planen diesen Ansatz auszuweiten und wollen speziell untersuchen, wie frühe Expositionen das Krankheitsrisiko Jahrzehnte später beeinflussen. Das Ziel sollte eine auf das individuelle Exposom und Genom abgestimmte Präzisionsmedizin sein.
[1] Patel, C.J., Ioannidis, J.P.A. & Manrai, A.K. An atlas of exposome–phenome associations in health and disease risk. Nat Med (2026). https://doi.org/10.1038/s41591-026-04266-0
[2] Patel C.J & Manray A.K., Development of exposome correlation globes to map out environment-wide associations. Pac Symp Biocomput. 2015 ; 20: 231–242.
Videos
- What is UK Biobank? UK Biobank. Video 2:23 min. https://www.youtube.com/watch?v=kTuiDadgcso&t=142s
- Chirag Patel: Exposome: decoding human health and diseases. TEDxSanFrancisco (31.10.2019) Video 17:13 min. https://www.youtube.com/watch?v=Pok6_ptvF-k&t=16s
- Printer-friendly version
- Log in to post comments